Homologia profunda

Na biologia evolutiva do desenvolvimento, o conceito de homologia profunda é utilizado para descrever casos em que os processos de crescimento e diferenciação celular são regulados por mecanismos genéticos que são homólogos e profundamente conservados em uma ampla gama de espécies.
História
Em 1822, o zoólogo francês Étienne Geoffroy Saint-Hilaire dissecou um lagostim e descobriu que seu corpo é organizado de maneira semelhante ao de um vertebrado, mas invertido dorsoventralmente [en]:[1]
Acabei de descobrir que todos os órgãos moles, isto é, os principais órgãos da vida, estão presentes nos crustáceos, e também nos insetos, na mesma ordem, nas mesmas relações e com o mesmo arranjo que seus análogos nos animais vertebrados superiores... Qual foi minha surpresa, e posso acrescentar, minha admiração, ao ver [tal] regra...[1]
A teoria de homologia de Geoffroy foi rejeitada pelo principal zoólogo francês de sua época, Georges Cuvier, mas, em 1994, demonstrou-se que Geoffroy estava correto. Em 1915, Santiago Ramón y Cajal mapeou as conexões neurais dos lobos ópticos de uma mosca, observando que elas se assemelhavam às dos vertebrados. Em 1978, Edward B. Lewis contribuiu para a fundação da biologia evolutiva do desenvolvimento ao descobrir que genes homeóticos regulam o desenvolvimento embrionário em moscas-das-frutas.[1]
Em 1997, o termo "homologia profunda" apareceu pela primeira vez em um artigo de Neil Shubin, Cliff Tabin e Sean B. Carroll, descrevendo a aparente relação nos aparelhos regulatórios genéticos que indicavam similaridades evolutivas em características animais distintas.[2]
Diferença em relação à homologia comum
Enquanto a homologia comum é observada no padrão de estruturas, como os ossos dos membros de mamíferos que são claramente relacionados, a homologia profunda pode se aplicar a grupos de animais com anatomias bastante distintas: vertebrados (com endoesqueletos de osso e cartilagem) e artrópodes (com exoesqueletos de quitina) possuem membros construídos usando "receitas" ou "algoritmos" semelhantes.[2][3][4][5]
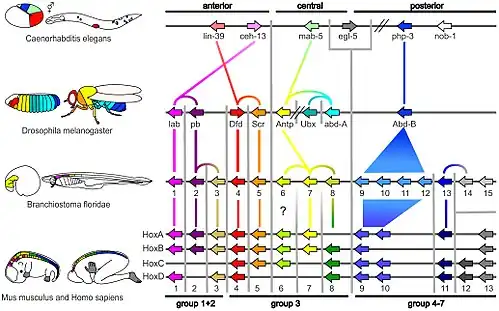
Nos metazoários, genes homeóticos controlam a diferenciação ao longo dos principais eixos corporais, e genes pax (especialmente o PAX6) auxiliam no controle do desenvolvimento dos olhos e outros órgãos sensoriais. A homologia profunda aplica-se a grupos amplamente separados, como nos olhos de mamíferos e nos olhos compostos, estruturalmente bastante diferentes, de insetos.[3]
Da mesma forma, genes hox contribuem para formar o padrão de segmentação de um animal. HoxA e HoxD, que regulam a formação de dedos em camundongos, controlam o desenvolvimento das nadadeiras raiadas em peixes-zebra; até então, essas estruturas eram consideradas não homólogas.[6]
Há uma possível homologia profunda entre animais que utilizam comunicação acústica, como aves e humanos, que podem compartilhar versões funcionais do gene FOXP2.[7]
Em células-tronco cancerígenas
Na biologia contemporânea, a compreensão da homologia profunda evoluiu para focar nos mecanismos moleculares e genéticos e suas funções, em vez de apenas na morfologia. As células-tronco cancerígenas (CSCs) são uma população de células dentro de um tumor capazes de se autorrenovar e se diferenciar em diversos tipos celulares, semelhantes às células-tronco normais. A teoria das células-tronco do câncer sugere que existe uma subpopulação de células, chamadas células-tronco cancerígenas, com características que as tornam únicas entre outros tipos de células em um câncer. Essas características incluem a capacidade de se multiplicar indefinidamente, resistência à quimioterapia e a possibilidade de serem responsáveis por recaídas após o tratamento.[8]
Ciclo de vida do câncer
O ciclo de vida unicelular do câncer e da Entamoeba apresenta semelhanças únicas, contradizendo a teoria filostratigráfica molecular para a origem do câncer.[9] Essa relação profunda entre os dois sistemas celulares é sustentada pelo "modelo ameba", que oferece uma compreensão mais ampla da biologia do câncer sob a perspectiva evolutiva.[10] O ciclo de vida G + S da Entamoeba é o ancestral comum mais próximo em comparação com outros ciclos de vida de organismos unicelulares. Ambos os sistemas celulares, ameba e câncer, utilizam o módulo genético G + S homólogo profundo, evoluído por um ancestral comum. Algumas semelhanças que compartilham são notavelmente próximas, incluindo:
- Uma linhagem germinativa assexuada reprodutiva capaz de formar células-tronco germinativas (GSCs, referidas como CSCs no câncer) e uma linhagem celular somática sem função reprodutiva de GSC;[11]
- Células germinativas e somáticas que proliferam por ciclos celulares assimétricos e simétricos e podem se interconverter por transições de germinativa para somática (GST) e de somática para germinativa (SGT); ambos os processos são chamados de MET e EMT no câncer;
- Linhagens germinativas sensíveis ao oxigênio que perdem irreversivelmente sua função reprodutiva devido a danos irreparáveis no DNA causados por excesso de oxigênio;
- Mecanismos de reparo de danos no DNA (DDR) para corrigir defeitos de replicação do DNA e poliploidização, mantendo a integridade genômica das GSCs/CSCs nascentes;
- Mecanismos de reparo de quebras de fita dupla no DNA via MGRS e estruturas PGCC, com ou sem fusão celular homóloga.[10]
Os MGRSs, conhecidos na terminologia médica como "células gigantes polipoides preexistentes (PGCCs)", são frequentemente observados em cancers não tratados. No câncer, o ciclo da linhagem germinativa reprodutiva começa com uma célula precursora que se poliploidiza dentro de um envelope celular. Essa linhagem germinativa do câncer passa por um processo de desenvolvimento semelhante ao da linhagem germinativa da Entamoeba. Um traço significativo de homologia profunda pode ser encontrado nas células-tronco germinativas de mamíferos. Com base em uma hipótese anterior, a linhagem germinativa é o ancestral comum nas linhagens de células-tronco somáticas. As GSCs filhas são as únicas células-tronco capazes de transmitir informação genética através das gerações.[10]
Algoritmo
Em 2010, uma equipe liderada por Edward Marcotte [en] desenvolveu um algoritmo que identifica módulos genéticos profundamente homólogos em organismos unicelulares, plantas e animais com base em fenótipos (como traços e defeitos de desenvolvimento). A técnica alinha fenótipos entre organismos com base na ortologia (um tipo de homologia) dos genes envolvidos nos fenótipos.[12][13]
Ver também
- Plano corporal - Conjunto de características morfológicas comuns aos membros de um filo de animais
Referências
- ↑ a b c Held, Lewis I. (Fevereiro de 2017). Deep Homology?: Uncanny Similarities of Humans and Flies Uncovered by Evo-Devo [Homologia Profunda?: Similaridades Impressionantes entre Humanos e Moscas Reveladas pela Evo-Devo]. [S.l.]: Cambridge University Press. pp. 2–5. ISBN 978-1316601211
- ↑ a b Shubin, Neil; Tabin, Cliff; Carroll, Sean (1997). «Fossils, genes and the evolution of animal limbs» [Fósseis, genes e a evolução dos membros animais]. Springer Nature. Nature. 388 (6643): 639–648. Bibcode:1997Natur.388..639S. PMID 9262397. doi:10.1038/41710

- ↑ a b Carroll, Sean B. (2006). Endless Forms Most Beautiful [Formas Infinitas Mais Belas]. [S.l.]: Weidenfeld & Nicolson. pp. 28, 66–69. ISBN 0-297-85094-6
- ↑ Gilbert, Scott F. (2000). «Homologous Pathways of Development». Developmental biology [Caminhos Homólogos do Desenvolvimento] 6ª ed. Sunderland, Mass: Sinauer Associates. ISBN 0-87893-243-7. Consultado em 14 de março de 2025
- ↑ Held, Lewis I. (Fevereiro de 2017). Deep Homology?: Uncanny Similarities of Humans and Flies Uncovered by Evo-Devo [Homologia Profunda?: Similaridades Impressionantes entre Humanos e Moscas Reveladas pela Evo-Devo]. [S.l.]: Cambridge University Press. pp. viii e ao longo do texto. ISBN 978-1316601211
- ↑ Zimmer, Carl (17 de agosto de 2016). «From Fins Into Hands: Scientists Discover a Deep Evolutionary Link» [De Nadadeiras a Mãos: Cientistas Descobrem uma Conexão Evolutiva Profunda]. The New York Times. Consultado em 14 de março de 2025
- ↑ Scharff, Petri; Constance, Jane (Julho de 2011). «Evo-Devo, Deep Homology and FoxP2: Implications for the Evolution of Speech and Language» [Evo-Devo, Homologia Profunda e FoxP2: Implicações para a Evolução da Fala e da Linguagem]. Philos. Trans. R. Soc. B. 366 (1574): 2124–2140. PMC 3130369
 . PMID 21690130. doi:10.1098/rstb.2011.0001
. PMID 21690130. doi:10.1098/rstb.2011.0001
- ↑ «Department of Cancer Biology - Cancer Stem Cells» [Departamento de Biologia do Câncer - Células-Tronco Cancerígenas]. Mayo Clinic (em inglês). Consultado em 14 de março de 2025
- ↑ Lineweaver, Charles H.; Davies, Paul C.W. (9 de junho de 2020). «Comparison of the Atavistic Model of Cancer to Somatic Mutation Theory: Phylostratigraphic Analyses Support the Atavistic Model». WORLD SCIENTIFIC: 243–261. ISBN 978-981-12-2348-8. doi:10.1142/9789811223495_0012. Consultado em 14 de março de 2025
- ↑ a b c Niculescu, Vladimir F. (4 de abril de 2022). «Cancer genes and cancer stem cells in tumorigenesis: Evolutionary deep homology and controversies» [Genes do câncer e células-tronco cancerígenas na tumorigênese: Homologia profunda evolutiva e controvérsias]. Genes & Diseases. 9 (5): 1234–1247. PMC 9293697
 . PMID 35873035. doi:10.1016/j.gendis.2022.03.010
. PMID 35873035. doi:10.1016/j.gendis.2022.03.010
- ↑ Spradling, Allan; Fuller, Margaret T; Braun, Robert E; Yoshida, Shosei (2011). «Germline Stem Cells». Cold Spring Harbor Perspectives in Biology (em inglês) (11). doi:10.1101/c. Consultado em 14 de março de 2025
- ↑ Zimmer, Carl (26 de abril de 2010). «The Search for Genes Leads to Unexpected Places» [A Busca por Genes Leva a Lugares Inesperados]. The New York Times. Consultado em 14 de março de 2025
- ↑ McGary, K. L.; Park, T. J.; Woods, J. O.; Cha, H. J.; Wallingford, J. B.; Marcotte, E. M. (Abril de 2010). «Systematic discovery of nonobvious human disease models through orthologous phenotypes» [Descoberta sistemática de modelos de doenças humanas não óbvios por meio de fenótipos ortólogos] (PDF). Proceedings of the National Academy of Sciences. 107 (14): 6544–9. Bibcode:2010PNAS..107.6544M. PMC 2851946
 . PMID 20308572. doi:10.1073/pnas.0910200107
. PMID 20308572. doi:10.1073/pnas.0910200107 . Consultado em 14 de março de 2025
. Consultado em 14 de março de 2025