Neofuncionalização
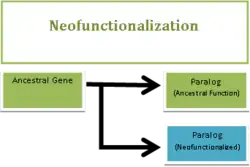
A neofuncionalização, um dos possíveis resultados da divergência funcional [en], ocorre quando uma cópia gênica, ou parálogo, assume uma função totalmente nova após um evento de duplicação cromossômica. A neofuncionalização é um processo de mutação adaptativa, o que significa que uma das cópias do gene deve sofrer mutações para desenvolver uma função que não estava presente no gene ancestral.[1][2][3] Em outras palavras, uma das duplicatas retém sua função original, enquanto a outra acumula alterações moleculares tais que, com o tempo, ela pode realizar uma tarefa diferente.[4]
O processo

O processo de neofuncionalização começa com um evento de duplicação cromossômica, que se acredita ocorrer como um mecanismo de defesa contra o acúmulo de mutações deletérias.[5][6][7] Após a duplicação, existem duas cópias idênticas do gene ancestral realizando exatamente a mesma função. Essa redundância permite que uma das cópias assuma uma nova função. Caso a nova função seja vantajosa, a seleção natural a seleciona positivamente e a nova mutação torna-se fixada na população.[3][8] A ocorrência da neofuncionalização pode, na maioria das vezes, ser atribuída a mudanças na região codificante ou nos elementos reguladores de um gene.[6] É muito mais raro observar mudanças profundas na função da proteína, como na estrutura da subunidade ou na afinidade com substratos e ligantes, como resultado direto da neofuncionalização.[6]
Restrições seletivas
A neofuncionalização também é comumente referida como "mutação durante a não funcionalidade" ou "mutação durante a redundância".[9] Independentemente de a mutação surgir após a perda de função de um gene ou devido a cópias gênicas redundantes, o aspecto crucial é que, em ambos os cenários, uma cópia do gene duplicado é liberada das restrições seletivas e, por acaso, adquire uma nova função, então aprimorada pela seleção natural.[6] Acredita-se que esse processo ocorra muito raramente na evolução por dois motivos principais. Primeiro, mudanças funcionais geralmente exigem um grande número de substituições de aminoácidos, o que possui baixa probabilidade de ocorrência. Segundo, como as mutações deletérias ocorrem com muito mais frequência do que as vantajosas, a probabilidade de que a função gênica seja perdida ao longo do tempo (ou seja, a pseudogenização) é muito maior do que a probabilidade de surgimento de uma nova função.[6][8] Walsh descobriu que a probabilidade relativa de neofuncionalização é determinada pela vantagem seletiva e pela taxa relativa de mutações vantajosas.[10] Isso foi demonstrado em sua derivação da probabilidade relativa de neofuncionalização em relação à pseudogenização, dada por: na qual ρ é a razão entre a taxa de mutação vantajosa e a taxa de mutação nula, e S é a seleção populacional 4NeS (Ne: tamanho efetivo populacional; S: intensidade da seleção).[10]
Modelo clássico
Em 1936, Hermann Muller propôs originalmente a neofuncionalização como um possível resultado de um evento de duplicação gênica.[11] Em 1970, Susumu Ohno [en] sugeriu que a neofuncionalização era o único mecanismo evolutivo que dava origem a novas funções gênicas em uma população.[6] Ele também acreditava que a neofuncionalização era a única alternativa à pseudogenização.[2] Tomoko Ohta (1987) foi uma das primeiras a sugerir que outros mecanismos poderiam existir para a preservação de genes duplicados na população.[6] Atualmente, a subfuncionalização [en] é um processo de fixação amplamente aceito para duplicatas gênicas e é o único outro resultado possível da divergência funcional.[2]
Neosubfuncionalização
A neosubfuncionalização ocorre quando a neofuncionalização é o resultado da subfuncionalização. Em outras palavras, após um evento de duplicação gênica formar parálogos que, após um período evolutivo, se subfuncionalizam, uma cópia do gene continua sua trajetória acumulando mutações que dão origem a uma nova função.[6][12] Alguns pesquisadores acreditam que a neofuncionalização é o estágio final para todos os genes subfuncionalizados. Por exemplo, de acordo com Rastogi e Liberles: "A neofuncionalização é o destino terminal de todas as cópias de genes duplicados retidas no genoma, e a subfuncionalização existe apenas como um estado transitório para preservar a cópia do gene duplicado".[2] Os resultados do estudo deles tornam-se mais evidentes à medida que o tamanho da população aumenta.
Exemplos
A evolução da proteína anticongelante [en] nos peixes antárticos da família Zoarcidae, como Lycodichthys [en] dearborni, oferece um exemplo clássico de neofuncionalização após duplicação gênica. No caso desses peixes, o gene da proteína anticongelante tipo III (AFPIII; P12102) divergiu de uma cópia paráloga do gene da ácido siálico sintase (sigla em inglês: SAS).[13] Descobriu-se que o gene SAS ancestral possuía tanto a função de sintase de ácido siálico quanto uma funcionalidade rudimentar de ligação ao gelo. Após a duplicação, um dos parálogos começou a acumular mutações que levaram à substituição dos domínios SAS do gene, permitindo o desenvolvimento e a otimização da função anticongelante.[13] O novo gene é agora capaz de promover a depressão não coligativa do ponto de congelamento, estando, portanto, neofuncionalizado.[13] Essa especialização permite que os peixes Zoarcidae sobrevivam nas temperaturas glaciais dos mares antárticos.
Outro exemplo diz respeito às proteínas opsinas sensíveis à luz nos olhos dos vertebrados, que permitem a visão de diferentes comprimentos de onda. Os vertebrados atuais possuem tipicamente quatro classes de opsinas de cones (LWS, SWS1, SWS2 e Rh2), bem como uma classe de opsina de bastonetes (rodopsina, Rh1), todas herdadas de ancestrais vertebrados primitivos. Essas cinco classes de opsinas visuais surgiram mediante uma série de duplicações gênicas, começando com a LWS e terminando com a Rh1.[14][15]
Limitações do modelo
Existem limitações na neofuncionalização como um modelo para divergência funcional, principalmente porque:
- A quantidade de mudanças de nucleotídeos que dão origem a uma nova função deve ser mínima; tornando a probabilidade de pseudogenização muito maior do que a de neofuncionalização após a duplicação.[6]
- Após a duplicação, ambas as cópias podem estar sujeitas a uma pressão seletiva equivalente àquela que restringia o gene ancestral; o que significa que nenhuma das cópias estaria livre para a neofuncionalização.[6]
- Em muitos casos, a seleção darwiniana positiva apresenta uma explicação mais parcimoniosa para a divergência de famílias multigênicas.[6]
Ver também
Referências
- ↑ Kleinjan DA, Bancewicz RM, Gautier P, Dahm R, Schonthaler HB, Damante G, et al. (fevereiro de 2008). «Subfunctionalization of duplicated zebrafish pax6 genes by cis-regulatory divergence». PLOS Genetics (em inglês). 4: e29. PMID 18282108. doi:10.1371/journal.pgen.03040029

- ↑ a b c d Rastogi S, Liberles DA (abril de 2005). «Subfunctionalization of duplicated genes as a transition state to neofunctionalization». BMC Evolutionary Biology (em inglês). 5 (1). 28 páginas. PMID 15831095. doi:10.1186/1471-21548-5-28
- ↑ a b Conrad B, Antonarakis SE (2007). «Gene duplication: a drive for phenotypic diversity and cause of human disease». Annual Review of Genomics and Human Genetics (em inglês). 8: 17–35. doi:10.1146/annurev.genom.8.0281307.1190233
- ↑ Evolution by Gene Duplication. (em inglês). New York, Heidelberg, Berlin: Springer-Verlag. 1970. pp. 59–87. ISBN 978-3-540-05225-8
- ↑ De Smet R, Van de Peer Y (abril de 2012). «Redundancy and rewiring of genetic networks following genome-wide duplication events». Current Opinion in Plant Biology (em inglês). 15 (2): 10 168–76. PMID 22305522
- ↑ a b c d e f g h i j k Graur D, Li WH (2000). Fundamentals of molecular evolution (em inglês) 2nd ed. Sunderland, Mass.: Sinauer Associates. ISBN 978-0-87893-266-5
- ↑ Amoutzias GD, He Y, Gordon J, Mossialos D, Oliver SG, Van de Peer Y (fevereiro de 2010). «Posttranslational regulation impacts the fate of duplicated genes». Proceedings of the National13 Academy of Sciences of the United States of America (em inglês). 107 (147): 2967–71. PMC 2840353
 . doi:10.1073/pnas.160911603107
. doi:10.1073/pnas.160911603107
- ↑ a b Innan H (setembro de 2009). «Population genetic models of duplicated genes». Genetica. 137 (1): 19–37. PMID 19266289. doi:10.1007/s10709-009-189355-1
- ↑ Hughes AL (1999). Adaptive evolution of genes and genomes (em inglês). New York: Oxford University Press. ISBN 978-0-19-511626-7
- ↑ a b Lynch M, Force A (janeiro de 2000). «The probability of duplicate gene preservation by subfunctionalization». Genetics (em inglês). 154 (1): 459–73. PMC 1460895
 . PMID 10629003. doi:10.1093/genetics/154.1.459
. PMID 10629003. doi:10.1093/genetics/154.1.459
- ↑ «Bar duplication». Science. 83 (2161): 528–30. Maio de 1936. Bibcode:1936Sci....83..528M. PMID 17806465
- ↑ He X, Zhang J (fevereiro de 2005). «Rapid subfunctionalization accompanied by prolonged and substantial neofunctionalization in duplicate gene evolution». Genetics (em inglês). 169 (2). PMC 1449125
 . PMID 15654095. doi:10.1534/genetics.104.037051
. PMID 15654095. doi:10.1534/genetics.104.037051
- ↑ a b c Deng C, Cheng CH, Ye H, He X, Chen L (dezembro de 2010). «Evolution of an antifreeze protein by neofunctionalization under escape from adaptive conflict». Proc22eedings of the National Academy of Sciences of the United23 States of America (em inglês). 107 (50). Bibcode:2010PNAS..10721593D. PMC 3003108
 . doi:10.1073/pnas.1007883107
. doi:10.1073/pnas.1007883107
- ↑ Hunt DM, Carvalho LS, Cowing JA, Davies WL (outubro de 2009). «Evolution and spectral tuning of visual pigments in birds and mammals». Philosophical Transactions of the Royal Society of London. Series B, Biological Sciences (em inglês). 364 (1531): 2941–2955. PMC 2781856
 . PMID 19720655. doi:10.1098/rstb.2009.0044
. PMID 19720655. doi:10.1098/rstb.2009.0044
- ↑ Trezise AE, Collin SP (outubro de 2005). «Opsins: evolution in waiting». Current Biology (em inglês). 15 (19): R794–R796. Bibcode:2005CBio...15.R794T. PMID 16213808. doi:10.1016/j.cub.2005.09.025
