Genética microbiana
Genética microbiana é uma área de estudo dentro da microbiologia e engenharia genética. A genética microbiana estuda microrganismos para diferentes propósitos. Os microrganismos observados são bactérias e arqueias. Alguns fungos e protozoários também são objetos de estudo nessa área. Os estudos de microrganismos envolvem estudos de genótipo e sistema de expressão. Genótipos são as composições herdadas de um organismo. A Engenharia Genética é um campo de trabalho e estudo dentro da genética microbiana.[1] A utilização da tecnologia do DNA recombinante é um processo deste trabalho.[1] O processo envolve a criação de moléculas de DNA recombinante por meio da manipulação de uma sequência de DNA.[1] O DNA criado fica então em contato com um organismo hospedeiro. A clonagem também é um exemplo de engenharia genética.[1]
Desde a descoberta dos microrganismos por Robert Hooke e Antoni van Leeuwenhoek durante o período de 1665-1885[2] eles têm sido usados para estudar muitos processos e têm tido aplicações em várias áreas de estudo em genética. Por exemplo: as taxas de crescimento rápido e os tempos de geração curtos dos microrganismos são usados pelos cientistas para estudar a evolução. As descobertas de Robert Hooke e Antoni van Leeuwenhoek envolveram representações, observações e descrições de microrganismos.[3] Mucor é o microfungo que Hooke apresentou e descreveu.[4] Sua contribuição foi o Mucor, o primeiro microrganismo a ser ilustrado. A contribuição de Antoni van Leeuwenhoek aos protozoários e bactérias microscópicas resultou em observações e descrições científicas.[4] Essas contribuições foram realizadas por um microscópio simples, o que levou à compreensão dos micróbios hoje e continua a progredir na compreensão dos cientistas.[5] A genética microbiana também tem aplicações na capacidade de estudar processos e vias semelhantes aos encontrados em humanos, como o metabolismo de medicamentos.[6]
Papel na compreensão da evolução
A genética microbiana pode se basear no trabalho de Charles Darwin, e os pesquisadores seguiram explorando suas teorias e conceitos por meio do uso de micróbios.[7] A teoria da seleção natural de Darwin, em particular, é uma fonte empregada. A pesquisa da evolução por meio da genética microbiana envolve cientistas em busca do equilíbrio evolutivo.[1] Um exemplo de como isso pode ser alcançado é por meio do estudo da seleção natural ou da deriva de micróbios.[7] A aplicação desse conhecimento decorre da investigação da presença ou ausência de diversas formas.[7] Os métodos envolvem a identificação de determinados trajetos, genes e funções. Após a observação do sujeito, o cientista pode compará-lo a uma sequência de gene conservada.[1] O processo de estudo da evolução microbiana desta forma não permite fornecer uma escala de tempo de quando a evolução ocorreu.[7] Entretanto, ao testar a evolução dessa maneira, os cientistas podem aprender as taxas e os resultados da evolução. O estudo da relação entre micróbios e o meio ambiente é um componente fundamental para a evolução da genética microbiana.[8]
Microrganismos cujo estudo é abrangido pela genética microbiana
Bactérias
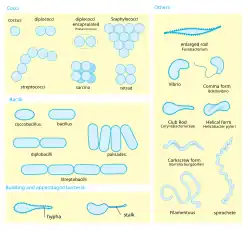
As bactérias existem neste planeta há aproximadamente 3,5 bilhões de anos e são classificadas por sua forma.[9] A genética bacteriana estuda os mecanismos de sua informação hereditária, seus cromossomos, plasmídeos, transposãos e fagos.[10]
Os mecanismos de transferência de genes amplamente investigados em bactérias englobam transformação genética, conjugação e transdução. A transformação natural é um mecanismo de adaptação bacteriana que permite a transferência de DNA de uma célula para outra por meio de um intermediário. A coleta do DNA do doador e sua integração recombinacional no cromossomo receptor dependem da expressão de diversos genes bacterianos, cujos produtos orientam essa operação.[11][12] De modo geral, a transformação é um processo de desenvolvimento complexo que demanda energia e aparenta ser uma adaptação para corrigir danos no DNA.[13]
Conjugação bacteriana é a transferência de material genético entre células bacterianas por contato direto de célula para célula ou por uma conexão semelhante a uma ponte entre duas células. A conjugação bacteriana foi extensivamente estudada em Escherichia coli, mas também ocorre em outras bactérias, como Mycobacterium smegmatis. A conjugação requer contato estável e prolongado entre uma cepa doadora e uma receptora, é resistente à DNase e o DNA transferido é incorporado ao cromossomo receptor por recombinação homóloga. A conjugação de E. coli é mediada pela expressão de genes de plasmídeo, enquanto a conjugação micobacteriana é mediada por genes no cromossomo bacteriano.[14]
Transdução é o processo pelo qual DNA estranho é introduzido em uma célula por um vírus ou vetor viral. Transdução é uma ferramenta comum usada por biólogos moleculares para introduzir de forma estável um gene estranho no genoma de uma célula hospedeira.[15][16]
Arqueia
Archaea é um domínio de organismos procariontes, unicelulares, que se acredita terem se desenvolvido há 4 bilhões de anos. "Eles não têm núcleo celular ou quaisquer outras organelas dentro de suas células". As arqueias se replicam assexuadamente em um processo conhecido como fissão binária. O ciclo de divisão celular inclui o momento em que os cromossomos das células-filhas se replicam. Como as arqueias têm uma estrutura cromossômica singular, as duas células-filhas se separam e a célula se divide. As arqueias têm motilidade, incluindo flagelos, que são estruturas semelhantes a caudas. Os cromossomos arqueanos replicam-se a partir de diferentes origens de replicação, produzindo duas células-filhas haplóides.[17] Eles compartilham um ancestral comum com as bactérias, mas estão mais intimamente relacionados aos eucariotos em comparação com as bactérias.[18] Algumas arqueia são capazes de sobreviver em ambientes extremos, o que leva a muitas aplicações no campo da genética. Uma dessas aplicações é o uso de enzimas arqueanas, que seriam mais capazes de sobreviver a condições adversas in vitro.[19]
A transferência de genes e a troca genética foram estudadas no arqueio halofílico Halobacterium volcanii e nos arqueios hipertermofílicos Sulfolobus solfataricus e Sulfolobus acidocaldarius. H. volcani forma pontes citoplasmáticas entre células que parecem ser usadas para transferência de DNA de uma célula para outra em qualquer direção.[20] Quando S. solfataricus e S. acidocaldarius são expostos a agentes que danificam o DNA, a agregação celular específica da espécie é induzida. A agregação celular medeia a troca de marcadores cromossômicos e a recombinação genética com alta frequência. Acredita-se que a agregação celular melhora a transferência de DNA específica da espécie entre as células Sulfolobus, a fim de proporcionar maior reparo do DNA danificado por meio de recombinação homóloga.[21][22][23] As arqueias são divididas em 3 subgrupos: halófilos, metanogênicos e termoacidófilos. O primeiro grupo, os metanógenos, são arqueiobactérias que vivem em pântanos e brejos, bem como no intestino dos humanos. Eles também desempenham um papel importante na decomposição e decaimento de organismos mortos. Metanógenos são organismos anaeróbicos que morrem quando expostos ao oxigênio. O segundo subgrupo de arqueiobactérias, os halófilos, são organismos presentes em áreas com alta concentração de sal, como o Grande Lago Salgado e o Mar Morto. O terceiro subgrupo, os termoacidófilos, também chamados de termófilos, são organismos que vivem em áreas ácidas. Eles estão presentes em áreas com baixos níveis de pH, como fontes termais e gêiseres. A maioria dos termófilos são encontrados no Parque Nacional de Yellowstone.[24]
A Genética Arqueana é o estudo de genes que consistem em células sem núcleo único.[25] As arqueias possuem um único cromossomo circular que contém múltiplas origens de replicação para o início da síntese de DNA.[26] A replicação do DNA de arqueia envolve processos semelhantes, incluindo iniciação, alongamento e terminação. A primase usada para sintetizar um primer de RNA varia daquela usada em eucariotos. A primase por arqueia é uma versão altamente derivada do motivo de reconhecimento de RNA (RRM).[26] As arqueias vêm de bactérias Gram positivas, que têm uma única bicamada lipídica e são resistentes a antibióticos. As arqueas são semelhantes às mitocôndrias dos eucariotos, pois liberam energia como trifosfato de adenosina (ATP) por meio de uma reação química chamada metabolismo.[26] Algumas arqueias conhecidas como arqueias fototróficas usam a energia do sol para produzir ATP. A ATP sintase é usada como fotofosforilação para converter produtos químicos em ATP.[17]
Arqueia e bactérias são estruturalmente semelhantes, embora não sejam intimamente relacionadas na árvore da vida. Os formatos das bactérias e das células das arqueias variam de um formato esférico conhecido como cocos até um formato de bastonete conhecido como bacilo. Eles também não possuem membrana interna e possuem parede celular que auxilia a célula a manter sua forma. Embora as células arqueanas tenham paredes celulares, elas não contêm peptidoglicano, o que significa que as arqueias não produzem celulose ou quitina. As arqueias são as mais intimamente relacionadas aos eucariotos devido ao tRNA presente nas arqueias, mas não nas bactérias. As arqueias têm os mesmos ribossomos que os eucariotos que sintetizam em proteínas.[27] Além da morfologia das arqueias e bactérias, existem outras diferenças entre esses domínios. Arqueias que vivem em ambientes extremos e hostis com baixos níveis de pH, como lagos salgados, oceanos e no intestino de ruminantes e humanos, também são conhecidas como extremófilas. Em contraste, as bactérias são encontradas em várias áreas, como plantas, animais, solo e rochas.[28]
Fungos
Os fungos podem ser organismos multicelulares ou unicelulares e se diferenciam de outros micróbios pela forma como adquirem nutrientes. Os fungos liberam enzimas ao seu redor para degradar a matéria orgânica.[9] A genética fúngica emprega leveduras e fungos filamentosos como organismos modelo para estudos genéticos em eucariotos, abrangendo a regulação do ciclo celular, a estrutura da cromatina e a regulação genética.[29]
Estudos do fungo Neurospora crassa contribuíram substancialmente para a compreensão de como os genes funcionam. N. crassa é um tipo de mofo vermelho do pão do filo Ascomycota. Ele é usado como organismo modelo porque é fácil de cultivar e tem um ciclo de vida haploide que torna a análise genética simples, já que características recessivas aparecerão na prole. A análise da recombinação genética é facilitada pelo arranjo ordenado dos produtos da meiose nos ascósporos. Em seu ambiente natural, N. crassa vive principalmente em regiões tropicais e subtropicais. Muitas vezes pode ser encontrado crescendo em matéria vegetal morta após incêndios.[30][31][32][33]
Neurospora foi usado por Edward Tatum e George Beadle em seus experimentos[34] pelos quais ganharam o Prêmio Nobel de Fisiologia ou Medicina em 1958. Os resultados desses experimentos levaram diretamente à hipótese de um gene-uma enzima, de que genes específicos codificam proteínas específicas. Este conceito provou ser o tiro de abertura para o que se tornou a genética molecular e todos os desenvolvimentos que se seguiram a partir daí.[35]
Saccharomyces cerevisiae é uma levedura do filo Ascomycota. Durante o crescimento vegetativo que normalmente ocorre quando os nutrientes são abundantes, S. cerevisiae se reproduz por mitose como células diplóides. Entretanto, quando privadas de alimento, essas células passam por meiose para formar esporos haplóides.[36] O acasalamento ocorre quando células haploides de tipos opostos de acasalamento, MATa e MATα, entram em contato. Ruderfer et al. apontaram que, na natureza, tais contatos são frequentes entre células de levedura intimamente relacionadas por duas razões. A primeira é que células de tipos opostos de acasalamento estão presentes juntas no mesmo acus, o saco que contém as células produzidas diretamente por uma única meiose, e essas células podem acasalar umas com as outras. A segunda razão é que células haploides de um tipo de acasalamento, após a divisão celular, geralmente produzem células do tipo de acasalamento oposto. Uma análise da ancestralidade das estirpes naturais de S. cerevisiae concluiu que o cruzamento ocorre muito raramente (apenas cerca de uma vez a cada 50.000 divisões celulares).[37] A relativa raridade na natureza dos eventos meióticos resultantes do cruzamento externo sugere que os possíveis benefícios a longo prazo do cruzamento externo (por exemplo, geração de diversidade) provavelmente não serão suficientes para manter o sexo de uma geração para a outra. Em vez disso, um benefício de curto prazo, como o reparo recombinacional meiótico de danos ao DNA causados por condições estressantes (como a fome) pode ser a chave para a manutenção do sexo em S. cerevisiae.[38]
Candida albicans é um fungo diploide que cresce tanto como levedura quanto como filamento. C. albicans é o patógeno fúngico mais comum em humanos. Ela causa infecções debilitantes nas mucosas e infecções sistêmicas potencialmente fatais. C. albicans manteve um elaborado, mas amplamente oculto, aparelho de acasalamento. Johnson sugeriu que as estratégias de acasalamento podem permitir que C. albicans sobreviva no ambiente hostil de um hospedeiro mamífero.[39]
Entre as 250 espécies conhecidas de aspergilli, cerca de 33% apresentam um estado sexual identificado.[40] Entre as espécies de Aspergillus que apresentam um ciclo sexual, a esmagadora maioria na natureza são homotálicas (autofecundantes).[40] A autofecundação no fungo homotálico Aspergillus nidulans envolve a ativação das mesmas vias de acasalamento características do sexo em espécies que se cruzam, ou seja, a autofecundação não ignora as vias necessárias para o sexo cruzado, mas requer a ativação dessas vias dentro de um único indivíduo.[41] A fusão de núcleos haploides ocorre dentro de estruturas reprodutivas denominadas cleistothecias, nas quais o zigoto diploide sofre divisões meióticas para produzir ascósporos haploides.[42]
Protozoários
Os protozoários são organismos unicelulares, que possuem núcleos e corpos celulares ultramicroscópicos em seu citoplasma.[9] Um aspecto particular dos protozoários que interessa aos geneticistas humanos são seus flagelos, que são muito semelhantes aos flagelos dos espermatozoides humanos.[43]
Estudos de Paramecium contribuíram para nossa compreensão da função da meiose. Como todos os ciliados, Paramecium tem um macronúcleo poliploide e um ou mais micronúcleos diploides. O macronúcleo controla funções celulares não reprodutivas, expressando os genes necessários para o funcionamento diário. O micronúcleo é o núcleo gerador, ou núcleo germinativo, que contém o material genético que é transmitido de uma geração para a seguinte.[44]
Na fase de fissão assexuada do crescimento, durante a qual as divisões celulares ocorrem por mitose em vez de meiose, ocorre o envelhecimento clonal, levando a uma perda gradual de vitalidade. Em algumas espécies, como a bem estudada Paramecium tetraurelia, a linhagem assexuada de paramécios que envelhecem clonalmente perde vitalidade e expira após cerca de 200 fissões se as células não passarem por meiose seguida de autogamia (autofertilização) ou conjugação (cruzamento externo). O dano ao DNA aumenta dramaticamente durante as sucessivas divisões clonais das células e é uma causa provável do envelhecimento clonal em P. tetraurelia.[45][46][47]
Quando P. tetraurelia envelhecida clonalmente é estimulada a passar por meiose em associação com autogamia ou conjugação, a progênie é rejuvenescida e consegue ter muito mais divisões de fissão binária mitótica. Durante qualquer um desses processos, os micronúcleos das células sofrem meiose, o macronúcleo antigo se desintegra e um novo macronúcleo é formado pela replicação do DNA micronuclear que havia sofrido meiose recentemente. Aparentemente, há pouco ou nenhum dano ao DNA no novo macronúcleo, sugerindo que o rejuvenescimento está associado ao reparo desses danos no micronúcleo durante a meiose.[48]
Vírus
Os vírus são organismos codificadores de capsídeos compostos de proteínas e ácidos nucleicos que podem se automontar após a replicação em uma célula hospedeira usando a maquinaria de replicação do hospedeiro.[49] Há um desacordo na ciência sobre se os vírus são vivos devido à falta de ribossomos. A compreensão do genoma viral é importante não apenas para estudos em genética, mas também para a compreensão de suas propriedades patogênicas.[50]
Muitos tipos de vírus são capazes de recombinação genética. Quando dois ou mais vírus individuais do mesmo tipo infectam uma célula, seus genomas podem se recombinar para produzir progênie viral recombinante. Tanto os vírus de DNA quanto os de RNA podem sofrer recombinação. Quando dois ou mais vírus, cada um contendo danos genômicos letais, infectam a mesma célula hospedeira, os genomas do vírus geralmente podem se emparelhar e passar por reparo recombinacional homólogo para produzir progênie viável.[51][52] Este processo é conhecido como reativação da multiplicidade.[51][53] As enzimas empregadas na reativação da multiplicidade são funcionalmente homólogas às enzimas empregadas no reparo recombinacional bacteriano e eucariótico. Foi descoberto que a reativação da multiplicidade ocorre com vírus patogênicos, incluindo o vírus da gripe, o HIV-1, o vírus adenovírus símio 40, o vírus da vacínia, o reovírus, o poliovírus e o vírus herpes simplex, bem como com numerosos bacteriófagos.[53]
Qualquer organismo vivo pode contrair um vírus dando aos parasitas a oportunidade de crescer. Os parasitas se alimentam dos nutrientes de outro organismo, o que permite que o vírus prospere. Uma vez que o corpo humano detecta um vírus, ele cria células de combate que atacam o parasita/vírus; literalmente, causando uma guerra dentro do corpo.[54] Um vírus pode afetar qualquer parte do corpo, causando uma ampla gama de doenças, como gripe, resfriado comum e doenças sexualmente transmissíveis.[54] A gripe é um vírus transmitido pelo ar que viaja por pequenas gotículas e é formalmente conhecido como Influenza. Parasitas viajam pelo ar e atacam o sistema respiratório humano. Pessoas que são inicialmente infectadas com esse vírus transmitem a infecção por meio de atividades normais do dia a dia, como falar e espirrar. Quando uma pessoa entra em contato com o vírus, diferentemente do resfriado comum, o vírus da gripe afeta as pessoas quase imediatamente. Os sintomas deste vírus são muito semelhantes aos do resfriado comum, mas muito piores. Dores no corpo, dor de garganta, dor de cabeça, suor frio, dores musculares e fadiga estão entre os muitos sintomas acompanhados pelo vírus.[55] Uma infecção viral no trato respiratório superior resulta no resfriado comum.[56] Com sintomas como dor de garganta, espirros, febre baixa e tosse, o resfriado comum geralmente é inofensivo e tende a desaparecer em cerca de uma semana. O resfriado comum também é um vírus que se espalha pelo ar, mas também pode ser transmitido por contato direto. Esta infecção demora alguns dias para desenvolver sintomas; é um processo gradual, ao contrário da gripe.[56]
Aplicações da genética microbiana
Os micróbios são ideais para estudos bioquímicos e genéticos e fizeram enormes contribuições para esses campos da ciência, como a demonstração de que o DNA é o material genético,[57][58] que o gene tem uma estrutura linear simples,[59] que o código genético é um código tripleto,[60] e que a expressão genética é regulada por processos genéticos específicos.[61] Jacques Monod e François Jacob usaram Escherichia coli, um tipo de bactéria, para desenvolver o modelo de operon de expressão genética, que estabelece a base da expressão e regulação genética.[62] Além disso, os processos hereditários dos microrganismos eucarióticos unicelulares são semelhantes aos dos organismos multicelulares, permitindo aos investigadores recolher também informações sobre este processo.[63] Outra bactéria que contribuiu muito para o campo da genética é a Thermus aquaticus, que é uma bactéria que tolera altas temperaturas. Deste micróbio, os cientistas isolaram a enzima Taq polimerase, que agora é usada na poderosa técnica experimental, a reação em cadeia da polimerase (PCR).[64] Além disso, o desenvolvimento da tecnologia do ADN recombinante através da utilização de bactérias levou ao nascimento da engenharia genética e da biotecnologia modernas.[9]
Utilizando micróbios, foram desenvolvidos protocolos para inserir genes em plasmídeos bacterianos, aproveitando sua rápida reprodução, para criar biofábricas para o gene de interesse. Essas bactérias geneticamente modificadas podem produzir produtos farmacêuticos como insulina, hormônio do crescimento humano, interferons e fatores de coagulação sanguínea.[9]
Os micróbios sintetizam uma variedade de enzimas para aplicações industriais, como alimentos fermentados, reagentes de testes de laboratório, produtos lácteos (como a renina) e até mesmo em roupas (como o fungo Trichoderma, cuja enzima é usada para dar aos jeans uma aparência de lavado a pedra).[9]
Atualmente, há potencial para que micróbios sejam usados como uma alternativa aos surfactantes à base de petróleo. Os surfactantes microbianos ainda teriam o mesmo tipo de grupos funcionais hidrofílicos e hidrofóbicos que seus equivalentes à base de petróleo, mas eles têm inúmeras vantagens sobre seus concorrentes. Em comparação, os compostos anfifílicos microbianos têm uma forte tendência a permanecer funcionais em ambientes extremos, como áreas com muito calor ou pH extremo, sendo ao mesmo tempo biodegradáveis e menos tóxicos para o meio ambiente. Este método de produção eficiente e barato pode ser a solução para o crescente consumo global de surfactantes. Ironicamente, a aplicação de surfactantes de base biológica com maior demanda é a indústria do petróleo, que utiliza surfactantes na produção geral, bem como no desenvolvimento de composições específicas de óleo.[65]
Os micróbios são uma fonte abundante de lipases, que têm uma ampla variedade de aplicações industriais e de consumo. As enzimas desempenham uma grande variedade de funções dentro das células dos seres vivos, então faz sentido que possamos usá-las para propósitos semelhantes em uma escala maior. As enzimas microbianas são normalmente preferidas para produção em massa devido à grande variedade de funções disponíveis e à sua capacidade de serem produzidas em massa. Enzimas vegetais e animais geralmente são caras demais para serem produzidas em massa, mas nem sempre esse é o caso. Especialmente em plantas. As aplicações industriais das lipases geralmente incluem a enzima como um catalisador mais eficiente e econômico na produção de produtos químicos comercialmente valiosos a partir de gorduras e óleos, porque elas são capazes de reter suas propriedades específicas em condições suaves e fáceis de manter e trabalham em uma taxa maior. Outras aplicações já bem-sucedidas de enzimas lipolíticas incluem a produção de biocombustíveis, polímeros, produtos farmacêuticos não estereoisoméricos, compostos agrícolas e compostos intensificadores de sabor.[66]
Em relação à otimização industrial, o benefício do método de produção de biofábrica é a capacidade de direcionar a otimização por meio da evolução direcionada. A eficiência e a especificidade da produção aumentarão ao longo do tempo pela imposição da seleção artificial. Esse método de melhoria da eficiência não é novidade na agricultura, mas é um conceito relativamente novo na produção industrial. Acredita-se que esse método será muito superior aos métodos industriais convencionais porque permite otimização em diversas frentes. A primeira frente é que os microrganismos que compõem as biofábricas podem evoluir de acordo com as nossas necessidades. A segunda frente é o método convencional de otimização proporcionado pela integração de tecnologias avançadas. Esta combinação de avanços convencionais e biológicos está apenas agora a ser utilizada e oferece um número virtualmente ilimitado de aplicações.[67]
Ver também
Notas
- Este artigo foi inicialmente traduzido, total ou parcialmente, do artigo da Wikipédia em inglês cujo título é «Microbial genetics».
Referências
- ↑ a b c d e f «Microbes and the Tools of Genetic Engineering | Microbiology». courses.lumenlearning.com. Consultado em 17 de novembro de 2018
- ↑ Gest, Hau (22 de maio de 2004). «The discovery of microorganisms by Robert Hooke and Antoni van Leeuwenhoek, Fellows of The Royal Society». Notes and Records of the Royal Society of London. 58 (2): 137–201. PMID 15209075. doi:10.1098/rsnr.2004.0055
- ↑ «BBC - History - Historic Figures: Antonie van Leeuwenhoek (1632 - 1723)». www.bbc.co.uk (em inglês). Consultado em 17 de novembro de 2018
- ↑ a b «antonie van leeuwenhoek: Topics by Science.gov». www.science.gov (em inglês). Consultado em 17 de novembro de 2018
- ↑ Mortlock, Robert (2013). Microorganisms As Model Systems for Studying Evolution. [S.l.]: Springer Verlag. ISBN 978-1-4684-4846-7
- ↑ Murphy, Cormac D. (2 de setembro de 2014). «Drug metabolism in microorganisms». Biotechnology Letters. 37 (1): 19–28. PMID 25179825. doi:10.1007/s10529-014-1653-8
- ↑ a b c d Buckley, Merry; Reid, Ann (2011). Microbial Evolution. [S.l.: s.n.]
- ↑ Chakraborty, Ranajit; Budowle, Bruce (2011). «Population Genetic Considerations in Statistical Interpretation of Microbial Forensic Data in Comparison with Human DNA Forensic Standard». Microbial Forensics. [S.l.: s.n.] pp. 561–580. ISBN 978-0-12-382006-8. doi:10.1016/B978-0-12-382006-8.00033-5
- ↑ a b c d e f Weeks, Benjamin S. (2012). Alcamo's microbes and society 3rd ed. Sudbury, MA: Jones & Bartlett Learning. ISBN 978-0-7637-9064-6
- ↑ «Bacterial genetics». Nature. Macmillan Publishers Limited. Consultado em 8 de novembro de 2015
- ↑ Chen I, Dubnau D (2004). «DNA uptake during bacterial transformation». Nature Reviews Microbiology. 2 (3): 241–9. PMID 15083159. doi:10.1038/nrmicro844
- ↑ Johnsborg O, Eldholm V, Håvarstein LS (2007). «Natural genetic transformation: prevalence, mechanisms and function». Research in Microbiology. 158 (10): 767–78. PMID 17997281. doi:10.1016/j.resmic.2007.09.004

- ↑ Michod RE, Bernstein H, Nedelcu AM (2008). «Adaptive value of sex in microbial pathogens». Infection, Genetics and Evolution. 8 (3): 267–85. PMID 18295550. doi:10.1016/j.meegid.2008.01.002
- ↑ Gray TA, Krywy JA, Harold J, Palumbo MJ, Derbyshire KM (2013). «Distributive conjugal transfer in mycobacteria generates progeny with meiotic-like genome-wide mosaicism, allowing mapping of a mating identity locus». PLOS Biology. 11 (7): e1001602. PMC 3706393
 . PMID 23874149. doi:10.1371/journal.pbio.1001602
. PMID 23874149. doi:10.1371/journal.pbio.1001602
- ↑ «Validation of Gene Transfection/Transduction - US». www.thermofisher.com (em inglês). Consultado em 14 de julho de 2025
- ↑ «transduction (prokaryotes) | Learn Science at Scitable». www.nature.com (em inglês). Consultado em 14 de julho de 2025
- ↑ a b Hogan, Michael. «What are Archaea? - Encyclopedia of Life». Encyclopedia of Life (em inglês)
- ↑ «Archaea». Microbe World. Consultado em 8 de novembro de 2015. Arquivado do original em 23 de novembro de 2015
- ↑ Chambers, Cecilia R.; Patrick, Wayne M. (2015). «Archaeal Nucleic Acid Ligases and Their Potential in Biotechnology». Archaea. 2015. 170571 páginas. PMC 4606414
 . PMID 26494982. doi:10.1155/2015/170571
. PMID 26494982. doi:10.1155/2015/170571
- ↑ Rosenshine I, Tchelet R, Mevarech M (1989). «The mechanism of DNA transfer in the mating system of an archaebacterium». Science. 245 (4924): 1387–9. Bibcode:1989Sci...245.1387R. PMID 2818746. doi:10.1126/science.2818746
- ↑ Fröls S, Ajon M, Wagner M, Teichmann D, Zolghadr B, Folea M, Boekema EJ, Driessen AJ, Schleper C, Albers SV (2008). «UV-inducible cellular aggregation of the hyperthermophilic archaeon Sulfolobus solfataricus is mediated by pili formation» (PDF). Molecular Microbiology. 70 (4): 938–52. PMID 18990182. doi:10.1111/j.1365-2958.2008.06459.x

- ↑ Fröls S, White MF, Schleper C (2009). «Reactions to UV damage in the model archaeon Sulfolobus solfataricus». Biochemical Society Transactions. 37 (Pt 1): 36–41. PMID 19143598. doi:10.1042/BST0370036
- ↑ Ajon M, Fröls S, van Wolferen M, Stoecker K, Teichmann D, Driessen AJ, Grogan DW, Albers SV, Schleper C (2011). «UV-inducible DNA exchange in hyperthermophilic archaea mediated by type IV pili» (PDF). Molecular Microbiology. 82 (4): 807–17. PMID 21999488. doi:10.1111/j.1365-2958.2011.07861.x

- ↑ «Archaebacteria Examples». BiologyWise. 3 de setembro de 2010. Consultado em 15 de julho de 2025
- ↑ «Archaeal genetics - Latest research and news». www.nature.com (em inglês). Consultado em 15 de julho de 2025
- ↑ a b c «Archaeal Genetics | Boundless Microbiology». courses.lumenlearning.com. Consultado em 15 de julho de 2025
- ↑ «Morphology of the Archaea». www.ucmp.berkeley.edu. Consultado em 15 de julho de 2025
- ↑ «Archaea vs Bacteria - Difference and Comparison». www.diffen.com (em inglês). Consultado em 15 de julho de 2025
- ↑ «Fungal Genetics». Nature.com. Macmillan Publishers Limited. Consultado em 9 de novembro de 2015
- ↑ Aramayo, Rodolfo; Selker, Eric U. (1 de outubro de 2013). «Neurospora crassa, a Model System for Epigenetics Research». Cold Spring Harbor Perspectives in Biology (em inglês) (10): a017921. ISSN 1943-0264. PMC 3783048
 . PMID 24086046. doi:10.1101/cshperspect.a017921. Consultado em 14 de julho de 2025
. PMID 24086046. doi:10.1101/cshperspect.a017921. Consultado em 14 de julho de 2025
- ↑ «Neurospora crassa». www.bionity.com. Consultado em 14 de julho de 2025
- ↑ «Neurospora crassa | EBSCO Research Starters». www.ebsco.com (em inglês). Consultado em 14 de julho de 2025
- ↑ Znameroski, Elizabeth A.; Glass, N. Louise (22 de janeiro de 2013). «Using a model filamentous fungus to unravel mechanisms of lignocellulose deconstruction». Biotechnology for Biofuels (1): 6. ISSN 1754-6834. PMC 3598899
 . doi:10.1186/1754-6834-6-6. Consultado em 14 de julho de 2025
. doi:10.1186/1754-6834-6-6. Consultado em 14 de julho de 2025
- ↑ Beadle GW, Tatum EL (1941). «Genetic Control of Biochemical Reactions in Neurospora». Proceedings of the National Academy of Sciences of the United States of America. 27 (11): 499–506. Bibcode:1941PNAS...27..499B. PMC 1078370
 . PMID 16588492. doi:10.1073/pnas.27.11.499
. PMID 16588492. doi:10.1073/pnas.27.11.499
- ↑ Horowitz NH, Berg P, Singer M, Lederberg J, Susman M, Doebley J, Crow JF (2004). «A centennial: George W. Beadle, 1903-1989». Genetics. 166 (1): 1–10. PMC 1470705
 . PMID 15020400. doi:10.1534/genetics.166.1.1
. PMID 15020400. doi:10.1534/genetics.166.1.1
- ↑ Herskowitz I (1988). «Life cycle of the budding yeast Saccharomyces cerevisiae». Microbiological Reviews. 52 (4): 536–53. PMC 373162
 . PMID 3070323. doi:10.1128/MMBR.52.4.536-553.1988
. PMID 3070323. doi:10.1128/MMBR.52.4.536-553.1988
- ↑ Ruderfer DM, Pratt SC, Seidel HS, Kruglyak L (2006). «Population genomic analysis of outcrossing and recombination in yeast». Nature Genetics. 38 (9): 1077–81. PMID 16892060. doi:10.1038/ng1859
- ↑ Birdsell, John A.; Wills, Christopher (2003). «The Evolutionary Origin and Maintenance of Sexual Recombination: A Review of Contemporary Models». Evolutionary Biology. [S.l.: s.n.] pp. 27–138. ISBN 978-1-4419-3385-0. doi:10.1007/978-1-4757-5190-1_2
- ↑ Johnson A (2003). «The biology of mating in Candida albicans». Nature Reviews Microbiology. 1 (2): 106–16. PMID 15035040. doi:10.1038/nrmicro752
- ↑ a b Dyer PS, O'Gorman CM (2012). «Sexual development and cryptic sexuality in fungi: insights from Aspergillus species». FEMS Microbiology Reviews. 36 (1): 165–92. PMID 22091779. doi:10.1111/j.1574-6976.2011.00308.x

- ↑ Paoletti M, Seymour FA, Alcocer MJ, Kaur N, Calvo AM, Archer DB, Dyer PS (2007). «Mating type and the genetic basis of self-fertility in the model fungus Aspergillus nidulans». Current Biology. 17 (16): 1384–9. PMID 17669651. doi:10.1016/j.cub.2007.07.012

- ↑ Gould, A. B. (1 de janeiro de 2009). Schaechter, Moselio, ed. «Fungi: Plant Pathogenic». Oxford: Academic Press: 457–477. ISBN 978-0-12-373944-5. Consultado em 14 de julho de 2025
- ↑ Pinskey, Justine M; Lagisetty, Adhya; Gui, Long; Phan, Nhan; Reetz, Evan; Tavakoli, Amirrasoul; Fu, Gang; Nicastro, Daniela (17 de novembro de 2022). Carter, Andrew P; Akhmanova, Anna; Brunet, Thibaut; Morriswood, Brooke, eds. «Three-dimensional flagella structures from animals' closest unicellular relatives, the Choanoflagellates». eLife: e78133. ISSN 2050-084X. doi:10.7554/eLife.78133. Consultado em 15 de julho de 2025
- ↑ Prescott DM (1994). «The DNA of ciliated protozoa». Microbiological Reviews. 58 (2): 233–67. PMC 372963
 . PMID 8078435. doi:10.1128/MMBR.58.2.233-267.1994
. PMID 8078435. doi:10.1128/MMBR.58.2.233-267.1994
- ↑ Smith-Sonneborn J (1979). «DNA repair and longevity assurance in Paramecium tetraurelia». Science. 203 (4385): 1115–7. Bibcode:1979Sci...203.1115S. PMID 424739. doi:10.1126/science.424739
- ↑ Holmes GE, Holmes NR (1986). «Accumulation of DNA damages in aging Paramecium tetraurelia». Molecular and General Genetics. 204 (1): 108–14. PMID 3091993. doi:10.1007/bf00330196
- ↑ Gilley D, Blackburn EH (1994). «Lack of telomere shortening during senescence in Paramecium». Proceedings of the National Academy of Sciences of the United States of America. 91 (5): 1955–8. Bibcode:1994PNAS...91.1955G. PMC 43283
 . PMID 8127914. doi:10.1073/pnas.91.5.1955
. PMID 8127914. doi:10.1073/pnas.91.5.1955
- ↑ Bernstein, Harris; Bernstein, Carol (11 de setembro de 2013). «Evolutionary Origin and Adaptive Function of Meiosis». IntechOpen (em inglês). ISBN 978-953-51-1197-9. doi:10.5772/56557. Consultado em 15 de julho de 2025
- ↑ Raoult, Didier; Forterre, Patrick (3 de março de 2008). «Redefining viruses: lessons from Mimivirus». Nature Reviews Microbiology. 6 (4): 315–319. PMID 18311164. doi:10.1038/nrmicro1858
- ↑ Seto, Donald (30 de novembro de 2010). «Viral Genomics and Bioinformatics». Viruses. 2 (12): 2587–2593. PMC 3185590
 . PMID 21994632. doi:10.3390/v2122587
. PMID 21994632. doi:10.3390/v2122587
- ↑ a b Bernstein C (1981). «Deoxyribonucleic acid repair in bacteriophage». Microbiological Reviews. 45 (1): 72–98. PMC 281499
 . PMID 6261109. doi:10.1128/MMBR.45.1.72-98.1981
. PMID 6261109. doi:10.1128/MMBR.45.1.72-98.1981
- ↑ Chen D, Bernstein C (1987). «Recombinational repair of hydrogen peroxide-induced damages in DNA of phage T4». Mutation Research. 184 (2): 87–98. PMID 3627145. doi:10.1016/0167-8817(87)90064-2
- ↑ a b Michod RE, Bernstein H, Nedelcu AM (maio de 2008). «Adaptive value of sex in microbial pathogens» (PDF). Infection, Genetics and Evolution. 8 (3): 267–85. PMID 18295550. doi:10.1016/j.meegid.2008.01.002
- ↑ a b Tennant, Paula (12 de março de 2018). Viruses : molecular biology, host interactions, and applications to biotechnology. San Diego, CA: [s.n.] ISBN 9780128111949. OCLC 1028979396
- ↑ Quinn, Tom (2008). Flu : a social history of influenza. London: New Holland. ISBN 9781845379414. OCLC 232713128
- ↑ a b Greenhough, Beth (6 de janeiro de 2012). «Where species meet and mingle: endemic human-virus relations, embodied communication and more-than-human agency at the Common Cold Unit 1946–90». Cultural Geographies (em inglês). 19 (3): 281–301. ISSN 1474-4740. doi:10.1177/1474474011422029

- ↑ Avery OT, MacLeod CM, McCarty M (1979). «Studies on the chemical nature of the substance inducing transformation of pneumococcal types. Inductions of transformation by a desoxyribonucleic acid fraction isolated from pneumococcus type III». Journal of Experimental Medicine. 149 (2): 297–326. PMC 2184805
 . PMID 33226. doi:10.1084/jem.149.2.297
. PMID 33226. doi:10.1084/jem.149.2.297
- ↑ Hershey AD, Chase M (1952). «Independent functions of viral protein and nucleic acid in growth of bacteriophage». Journal of General Physiology. 36 (1): 39–56. PMC 2147348
 . PMID 12981234. doi:10.1085/jgp.36.1.39
. PMID 12981234. doi:10.1085/jgp.36.1.39
- ↑ Benzer S (1959). «On The Topology of the Genetic Fine Structure». Proceedings of the National Academy of Sciences of the United States of America. 45 (11): 1607–20. Bibcode:1959PNAS...45.1607B. PMC 222769
 . PMID 16590553. doi:10.1073/pnas.45.11.1607
. PMID 16590553. doi:10.1073/pnas.45.11.1607
- ↑ Crick FH, Barnett L, Brenner S, Watts-Tobin RJ (1961). «General nature of the genetic code for proteins». Nature. 192 (4809): 1227–32. Bibcode:1961Natur.192.1227C. PMID 13882203. doi:10.1038/1921227a0
- ↑ Jacob F, Monod J (1961). «Genetic regulatory mechanisms in the synthesis of proteins». Journal of Molecular Biology. 3 (3): 318–56. PMID 13718526. doi:10.1016/S0022-2836(61)80072-7
- ↑ «Microbial Genetics». World of Microbiology and Immunology. 2003. Consultado em 9 de novembro de 2015
- ↑ Bainbridge, B.W. (1987). Genetics of microbes 2nd ed. Glasgow: Blackie. ISBN 978-0-412-01281-5
- ↑ Terpe, Kay (1 de novembro de 2013). «Overview of thermostable DNA polymerases for classical PCR applications: from molecular and biochemical fundamentals to commercial systems». Applied Microbiology and Biotechnology. 97 (24): 10243–10254. PMID 24177730. doi:10.1007/s00253-013-5290-2
- ↑ Banat, I. M.; Makkar, R. S.; Cameotra, S. S. (15 de maio de 2000). «Potential commercial applications of microbial surfactants». Applied Microbiology and Biotechnology (em inglês). 53 (5): 495–508. ISSN 0175-7598. PMID 10855707. doi:10.1007/s002530051648
- ↑ Hasan, Fariha; Shah, Aamer Ali; Hameed, Abdul (26 de junho de 2006). «Industrial applications of microbial lipases». Enzyme and Microbial Technology (em inglês). 39 (2): 235–251. ISSN 0141-0229. doi:10.1016/j.enzmictec.2005.10.016
- ↑ Kondo, Akihiko; Ishii, Jun; Hara, Kiyotaka Y.; Hasunuma, Tomohisa; Matsuda, Fumio (20 de janeiro de 2013). «Development of microbial cell factories for bio-refinery through synthetic bioengineering». Journal of Biotechnology (em inglês). 163 (2): 204–216. ISSN 0168-1656. PMID 22728424. doi:10.1016/j.jbiotec.2012.05.021