Despurinação
A despurinação é uma reação química dos desoxirribonucleosídeos purínicos, desoxiadenosina e desoxiguanosina, e dos ribonucleosídeos adenosina ou guanosina, na qual a sua ligação β-N-glicosídica é clivada hidroliticamente libertando uma base nitrogenada, adenina ou guanina, respetivamente. O segundo produto da despurinação de desoxirribonucleósidos e ribonucleósidos é um açúcar 2’-desoxirribose e ribose, respetivamente. Compostos mais complexos que contêm resíduos de nucleósidos, como os nucleótidos e os ácidos nucleicos, também sofrem despurinação. Os desoxirribonucleósidos e os seus derivados têm uma tendência substancialmente maior à despurinação do que os seus correspondentes ribonucleósidos equivalentes. A perda de bases pirimidínicas (citosina e timina) ocorre por mecanismos similares, mas a uma taxa muito inferior.
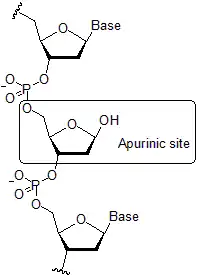
Quando a despurinação ocorre no ADN origina a formação de um sítio apurínico e causa uma alteração da sua estrutura. Os estudos estimam que numa célula humana típica se perdem deste modo cerca de 5.000 purinas por dia.[1] Nas células, uma das principais causas da despurinação é a presença de metabólitos endógenos que causam reações químicas. Os sítios apurínicos no ADN bicatenário são reparados eficientemente por uma porção da via de reparação por excisão de bases (BER). As bases despurinadas no ADN de fita simples que são replicadas podem originar mutações, porque na ausência de informação da fita complementar, a reparação por excisão de bases pode adicionar uma base incorreta a um sítio apurínico, o que causa uma mutação por transição ou transversão.[2] A despurinação desempenha um papel principal na iniciação do cancro.[3] A despurinação hidrolítica é uma das principais formas de danos que se observam no ADN antigo encontrado em material fóssil e subfóssil, uma vez que as bases permanecem sem reparação. Isto resulta tanto em perdas de informação (a sequência de bases), como em dificuldades para a recuperação e replicação in vitro dessas moléculas antigas danificadas pela aplicação da técnica da reação em cadeia da polimerase.
Química da reação
A despurinação não é rara porque a purina é um bom grupo de saída devido ao seu nitrogénio na posição 9 (ver estrutura de uma purina). Além disso, o carbono anomérico é especialmente reativo nas substituições nucleofílicas (tornando a ligação carbono-oxigénio mais curta, mais forte e mais polar, enquanto a ligação carbono-purina se torna mais longa e fraca). Isto torna a ligação especialmente suscetível à hidrólise. Em síntese química de oligonucleótidos, a despurinação é um dos principais fatores que limitam o comprimento dos oligonucleótidos sintéticos.[4]
Referências
- ↑ Lindahl, T. (22 de abril de 1993). «Instability and decay of the primary structure of DNA». Nature. 362 (6422): 709–715. ISSN 0028-0836. PMID 8469282. doi:10.1038/362709a0
- ↑ Carr, Steven M. (2009). «Depurination produces transversion mutations». mun.ca. Memorial University of Newfoundland. Consultado em 19 de agosto de 2010
- ↑ Cavalieri, E.; Saeed, M.; Zahid, M.; Cassada, D.; Snow, D.; Miljkovic, M.; Rogan, E. (2012). «Mechanism of DNA depurination by carcinogens in relation to cancer initiation.». IUBMB Life. 64 (2): 169–179. doi:10.1002/iub.586
- ↑ Le Proust, E. M.; Peck, B. J.; Spirin, K.; McCuen, Heather B.; Moore, B.; Namsaraev, E.; Caruthers, M. H. (2010). «Synthesis of high-quality libraries of long (150mer) oligonucleotides by a novel depurination controlled process.». Nucleic Acids Res. 38 (8): 2522–2540. doi:10.1093/nar/gkq163