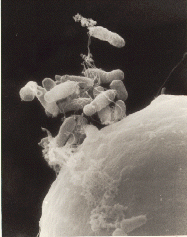
Agrobacterium tumefaciens
Agrobacterium tumefaciens
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
 | |||||||||||||||
| Classificação científica | |||||||||||||||
| |||||||||||||||
| Nome binomial | |||||||||||||||
| Agrobacterium tumefaciens (Smith & Townsend, 1907) Conn, 1942 | |||||||||||||||
| Sinónimos | |||||||||||||||
| Rhizobium radiobacter (Beijerinck and van Delden, 1902) Young et al., 2001 | |||||||||||||||
Agrobacterium tumefaciens[1] (também conhecida como Rhizobium radiobacter) é uma espécie de bactéria de solo gram-negativa causadora da doença da galha da coroa (tumores) em mais de 140 espécies de eudicotiledôneas. Os sintomas são causados pela inserção de um pequeno segmento de DNA (conhecido como T-DNA), de um plasmídeo na célula vegetal,[2] que é incorporado em um local semi-aleatório no genoma da planta. Constataram-se, assim, que genomas de plantas podem ser melhorados geneticamente por meio do uso de Agrobacterium na inserção de genes desejáveis de seu T-DNA no da planta hospedeira.[3]
Descrição
Agrobacterium tumefaciens é uma Alphaproteobacteria gram-negativa, em formato de bacilo da família Rhizobiaceae, que inclui as bactérias fixadoras de nitrogênio. Ao contrário das bactérias pertencentes ao género Rhizobium, as espécies Agrobacterium são patogênicas. As espécies de plantas mais afetadas são: nogueiras, videiras e algumas plantas da ordem Caryophyllales, como a beterraba e o ruibarbo.[4][5]
Método de infecção
A Agrobacterium tumefaciens infecta a planta através de seu plasmídeo Ti. O plasmídeo Ti incorpora um segmento de seu DNA, conhecido como DNA de transferência ou T-DNA, no DNA cromossômico das células vegetais. A bactéria também possui flagelos que lhe permitem locomover pelo solo em direção aos fotoassimilados que se acumulam na rizosfera. Algumas cepas podem se mover quimiotaticamente em direção a exsudatos químicos de plantas, como acetoseringona e açúcares, o que indica a presença de uma ferida na planta por onde a bactéria pode penetrar. Os compostos fenólicos são reconhecidos pela proteína VirA, uma proteína transmembrana codificada no gene virA no plasmídeo Ti. Os açúcares são reconhecidos pela proteína chvE, uma proteína codificada por genes cromossômicos localizada no periplasma.[6]
Pelo menos 25 genes vir no plasmídeo Ti são necessários para a indução do tumor.[7] A proteína VirA tem atividade de auto cinase: ela se fosforila em um resíduo de histidina. Em seguida, a proteína VirA fosforila a proteína VirG em seu resíduo de aspartato. A proteína virG é uma proteína citoplasmática produzida a partir do gene do plasmídeo Ti virG. É um fator de transcrição, induzindo a transcrição dos operons vir. A proteína ChvE regula o segundo mecanismo de ativação dos genes vir. Aumenta a sensibilidade da proteína VirA aos compostos fenólicos.[8]
A anexação é um processo de duas etapas. Após uma ligação inicial fraca e reversível, as bactérias sintetizam fibrilas de celulose que as ancoram à célula vegetal para a qual foram atraídas. Quatro genes principais estão envolvidos neste processo: chvA, chvB, pscA e att. Essas fibrilas também ancoram as bactérias umas às outras, ajudando a formar uma microcolônia.[carece de fontes]
Após a produção de fibrilas de celulose, uma proteína de membrana externa dependente de cálcio chamada ricadesina é produzida, o que também auxilia na adesão das bactérias à parede celular. Atualmente, existem vários relatórios sobre a padronização do protocolo para a transformação mediada por Agrobacterium. O efeito de diferentes parâmetros como tempo de infecção, acetoseringona, DTT e cisteína foram estudados na soja (Glycine max).[9]
Uso na biotecnologia
As capacidades de transmissão de DNA do Agrobacterium têm sido amplamente estudadas na biotecnologia como um meio de inserção de novos genes em espécies de plantas. Os biólogos Marc Van Montagu e Jeff Schell descobriram o mecanismo de transferência de genes entre Agrobacterium e plantas hospedeiras, o que resultou no desenvolvimento de métodos para alterar o genótipo da bactéria através da técnica de engenharia genética em plantas.[10] Uma porção do DNA plasmidial é transferido para a planta através da prática de clonagem de uma sequência genética, que será usada para incorporar um gene de interesse no genoma da célula vegetal.[11] Este processo foi realizado usando o gene da luciferase para produzir plantas fluorescentes.[12] Esta luminescência tem sido um dispositivo útil no estudo da função do cloroplasto vegetal e como um gene repórter.[12] Também é possível transformar Arabidopsis thaliana mergulhando flores em uma calda de Agrobacterium: a semente produzida será transgênica. Em condições de laboratório, o T-DNA também foi transferido para células humanas, demonstrando a diversidade de aplicações de inserção.[13]
Referências
- ↑ «Taxonomy browser (Agrobacterium tumefaciens)». National Center for Biotechnology Information. Consultado em 7 de janeiro de 2024
- ↑ Chilton, Mary-Dell; Drummond, Martin H.; Merlo, Donald J.; Sciaky, Daniela; Montoya, Alice L.; Gordon, Milton P.; Nester, Eugene W. (Junho de 1977). «Stable incorporation of plasmid DNA into higher plant cells: the molecular basis of crown gall tumorigenesis». Cell. 11 (2): 263–271. ISSN 0092-8674. PMID 890735. doi:10.1016/0092-8674(77)90043-5
- ↑ J. B. Brown, Pamela; H. Chang, Jeff; Fuqua, Clay (25 de abril de 2023). «Agrobacterium tumefaciens: a Transformative Agent for Fundamental Insights into Host-Microbe Interactions, Genome Biology, Chemical Signaling, and Cell Biology». PMID 36892285. doi:10.1128/jb.00005-23. Consultado em 25 de abril de 2025
- ↑ Moore LW, Chilton WS, Canfield ML (Janeiro de 1997). «Diversity of opines and opine-catabolizing bacteria isolated from naturally occurring crown gall tumors». Applied and Environmental Microbiology. 63 (1): 201–7. Bibcode:1997ApEnM..63..201M. PMC 1389099
 . PMID 16535484. doi:10.1128/AEM.63.1.201-207.1997
. PMID 16535484. doi:10.1128/AEM.63.1.201-207.1997
- ↑ «Crown Galls». Missouri Botanical Garden. Consultado em 2 de dezembro de 2019
- ↑ Gelvin, Stanton B (Março de 2003). «Agrobacterium-mediated plant transformation: the biology behind the "gene-jockeying" tool». Microbiology and Molecular Biology Reviews. 67 (1): 16–37, table of contents. PMC 150518
 . PMID 12626681. doi:10.1128/mmbr.67.1.16-37.2003
. PMID 12626681. doi:10.1128/mmbr.67.1.16-37.2003
- ↑ Winans, Stephen C. (1992). «Two-way chemical signaling in Agrobacterium-plant interactions». Microbiological Reviews (em inglês). 56 (1): 12–31. ISSN 0146-0749. PMC 372852
 . PMID 1579105. doi:10.1128/mr.56.1.12-31.1992
. PMID 1579105. doi:10.1128/mr.56.1.12-31.1992
- ↑ Gelvin, Stanton B (Março de 2003). «Agrobacterium-mediated plant transformation: the biology behind the "gene-jockeying" tool». Microbiology and Molecular Biology Reviews. 67 (1): 16–37, table of contents. PMC 150518
 . PMID 12626681. doi:10.1128/mmbr.67.1.16-37.2003
. PMID 12626681. doi:10.1128/mmbr.67.1.16-37.2003
- ↑ Barate PL, Kumar RR, Waghmare SG, Pawar KR, Tabe RH (2018). «Effect of different parameters on Agrobacterium mediated transformation in Glycine max». International Journal of Advanced Biological Research. 8 (1): 99–105
- ↑ Schell, J.; Van Montagu, M. (1977). «The Ti-Plasmid of Agrobacterium Tumefaciens, A Natural Vector for the Introduction of NIF Genes in Plants?». In: Hollaender; Burris; Day; Hardy. Genetic Engineering for Nitrogen Fixation. Col: Basic Life Sciences. 9. [S.l.: s.n.] pp. 159–79. ISBN 978-1-4684-0882-9. PMID 336023. doi:10.1007/978-1-4684-0880-5_12
- ↑ Zambryski P, Joos H, Genetello C, Leemans J, Montagu MV, Schell J (1983). «Ti plasmid vector for the introduction of DNA into plant cells without alteration of their normal regeneration capacity». The EMBO Journal. 2 (12): 2143–50. PMC 555426
 . PMID 16453482. doi:10.1002/j.1460-2075.1983.tb01715.x
. PMID 16453482. doi:10.1002/j.1460-2075.1983.tb01715.x
- ↑ a b Root M (1988). «Glow in the dark biotechnology». BioScience. 38 (11): 745–747. JSTOR 1310781. doi:10.2307/1310781
- ↑ Kunik T, Tzfira T, Kapulnik Y, Gafni Y, Dingwall C, Citovsky V (Fevereiro de 2001). «Genetic transformation of HeLa cells by Agrobacterium». Proceedings of the National Academy of Sciences of the United States of America. 98 (4): 1871–6. Bibcode:2001PNAS...98.1871K. PMC 29349
 . PMID 11172043. doi:10.1073/pnas.041327598
. PMID 11172043. doi:10.1073/pnas.041327598
Ligações externas
 Media relacionados com Agrobacterium tumefaciens no Wikimedia Commons
Media relacionados com Agrobacterium tumefaciens no Wikimedia Commons- "Agrobacterium fabrum" C58 Genome Page — as sequenced by Cereon Genomics/University of Richmond