Virófago
| Família Lavidaviridae | |
|---|---|

| |
| Sputnik (vírus) | |
| Classificação viral | |
| Gêneros e espécies | |
|
Virofagos são pequenos vírus com DNA de fita dupla que requerem a co-infecção com outro vírus, geralmente um vírus gigante. Eles dependem da fábrica de replicação do vírus gigante e apresentam relação parasitária com este, podendo inibir sua replicação e melhorar a sobrevivência do hospedeiro. Formam a classe Virophaviricetes.
Descoberta
O primeiro virofago, o Sputnik, foi descoberto em 2008 numa torre de resfriamento em Paris, co-infectando com o mamavírus. Outros virofagos incluem Sputnik 2, Sputnik 3, Zamilon e Mavirus.[1][2]
Gama de hospedeiros e replicação
Virofagos só se replicam na presença de vírus gigantes, pois não possuem enzimas próprias. Usam a maquinaria de transcrição do vírus co-infectante, e não da célula hospedeira.
Genoma
Possuem genomas de DNA de fita dupla, circulares ou lineares, entre 17 e 30 kbp. A cápside icosaédrica mede de 40 a 80 nm.[3][4]
| Vírus | Tamanho do genoma (kbp) | Tamanho da partícula (nm) |
|---|---|---|
| Poliovírus | 7 | 30 |
| Adenovírus | 26–48 | 90–100 |
| Virofago Zamilon | 17 | 50–60 |
| Virofago Sputnik | 18 | 74 |
| Vírus gigante Cafeteria roenbergensis | 700 | 75 |
| Mimivírus | 1.181 | 400–800 |
Todos os virofagos conhecidos possuem quatro genes centrais: proteínas de cápside (maior e menor), protease cisteína (PRO) e ATPase de empacotamento de DNA.[5]
Taxonomia
A classe Virophaviricetes (chamada Maveriviricetes até 2024) inclui quatro ordens:[6]
- Classe: Virophaviricetes
- Ordem: Divpevirales
- Família: Ruviroviridae
- Gênero: Oviruvirus
- Família: Ruviroviridae
- Ordem: Lavidavirales
- Família: Maviroviridae
- Gênero: Mavirus
- Família: Maviroviridae
- Ordem: Mividavirales
- Família: Sputniviroviridae
- Gênero: Sputnikvirus
- Família: Sputniviroviridae
- Ordem: Priklausovirales
- Ordem: Divpevirales
Análises metagenômicas identificaram 328 genomas de virofagos de alta qualidade e os agruparam em 27 clados distintos com genomas semelhantes.[7]
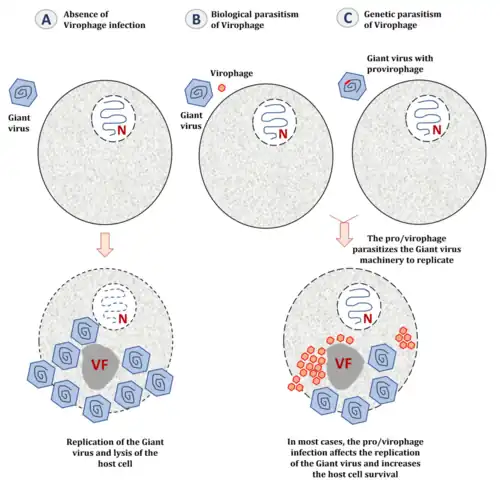
(B) Quando a célula é co-infectada com um vírus gigante e um virofago, o virofago parasita a fábrica viral do vírus gigante, reduzindo sua replicação e aumentando a sobrevivência da célula hospedeira.
(C) Quando o genoma do vírus gigante é parasitado por um provirofago, este é expresso durante a replicação, inibindo o vírus gigante e favorecendo a sobrevivência celular.
FV: Fábrica viral
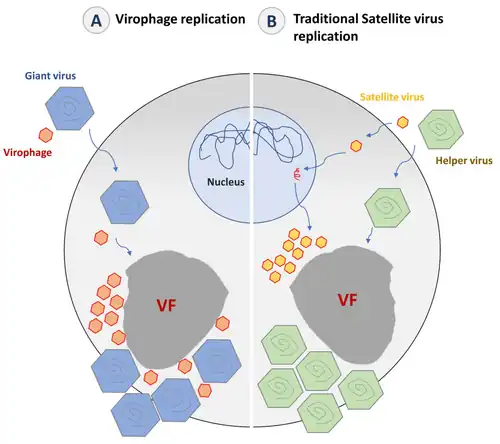
(B) Vírus satélites iniciam a replicação no núcleo com maquinaria da célula hospedeira e, no citoplasma, usam a morfogênese do vírus auxiliar para formar seus vírions.
Referências
- ↑ Fischer, M. G.; Suttle, C. A. (2011). “A virophage at the origin of large DNA transposons”. Science, 332(6026): 231–234. doi:10.1126/science.1199412. PMID 21385722.
- ↑ Fischer, M. G.; Hackl, T. (2016). “Host genome integration and giant virus–induced reactivation of the virophage mavirus”. Nature, 540(7632): 288–291. doi:10.1038/nature20593. PMID 27929021.
- ↑ Katzourakis, A.; Aswad, A. (2014). “The origins of giant viruses, virophages and their relatives in host genomes”. BMC Biology, 12: 2–3. doi:10.1186/s12915-014-0051-y. PMID 25184667.
- ↑ Krupovic, M.; Kuhn, J. H.; Fischer, M. G. (2015). “A classification system for virophages and satellite viruses”. Archives of Virology, 161(1): 233–247. doi:10.1007/s00705-015-2622-9. PMID 26446887.
- ↑ Paez-Espino, D.; Zhou, J.; Roux, S.; Nayfach, S.; Pavlopoulos, G. A.; Schulz, F.; McMahon, K. D.; Walsh, D.; Woyke, T.; Ivanova, N. N.; Eloe-Fadrosh, E. A.; Tringe, S. G.; Kyrpides, N. C. (2019). “Diversity, evolution, and classification of virophages uncovered through global metagenomics”. Microbiome, 7(1): 157. doi:10.1186/s40168-019-0768-5. PMID 31823797.
- ↑ «Histórico do táxon: Classe: Virophaviricetes (2024 Release)». International Committee on Taxonomy of Viruses. Consultado em 16 março 2025
- ↑ Paez-Espino, D.; Zhou, J.; Roux, S.; Nayfach, S.; Pavlopoulos, G. A.; Schulz, F.; McMahon, K. D.; Walsh, D.; Woyke, T.; Ivanova, N. N.; Eloe-Fadrosh, E. A.; Tringe, S. G.; Kyrpides, N. C. (2019). “Diversity, evolution, and classification of virophages uncovered through global metagenomics”. Microbiome, 7(1): 157. doi:10.1186/s40168-019-0768-5. PMID 31823797.
- ↑ a b Mougari, S.; Sahmi-Bounsiar, D.; Levasseur, A.; Colson, P.; La Scola, B. (2019). “Virophages of Giant Viruses: An Update at Eleven”. Viruses, 11(8): 733. doi:10.3390/v11080733.