Bacteriófago MS2
| ERRO: parâmetro(s) nomeando o táxon está incorrecto; ver documentação | |
|---|---|
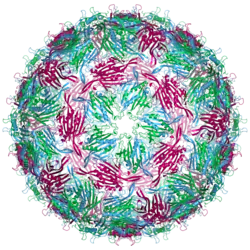
| |
| Bacteriophage MS2 capsid structure. The three quasi-equivalent conformers are labelled blue (chain a), green (chain b) and magenta (chain c) | |
| Classificação viral |
O bacteriófago MS2 ( Emesvirus zinderi ), comumente chamado de MS2, é um vírus icosaédrico de RNA de fita simples de sentido positivo que infecta a bactéria Escherichia coli e outros membros da família Enterobacteriaceae.[1] O MS2 é um membro duma família de vírus bacterianos intimamente relacionados que inclui o bacteriófago f2, o bacteriófago Qβ, o R17 e o GA.[2][3]
É pequeno e contém uma proteína de maturação, uma proteína de revestimento e RNA genómico. Possui também um dos genomas mais pequenos conhecidos, codificando quatro proteínas.
O ciclo de vida do MS2 envolve a infeção das bactérias com o fator de fertilidade, permitindo que o vírus se ligue aos pili, embora o mecanismo pelo qual o RNA viral entra na bactéria permaneça desconhecido. Uma vez dentro da bactéria, o RNA viral começa a funcionar como um RNA mensageiro para produzir proteínas virais. O MS2 replica o seu genoma de cadeia positiva criando um RNA de cadeia negativa como molde. O vírus monta-se então e a célula bacteriana sofre lise, libertando novos vírus.
Virologia
Genoma

| Gene | Tamanho | Produto do gene | aa |
|---|---|---|---|
| esteira
(MS2g1) |
1487 nt | maturação | 393 |
| cp
(MS2g2) |
510 nt | proteína de revestimento | 130 |
| lys
(MS2g3) |
295 nt | proteína de lise | 75 |
| representante
(MS2g4) |
2055 nt | Replicase de RNA , | 545 |
O genoma do MS2 é um dos menores conhecidos, consistindo em 3569 nucleotídeos de RNA de fita simples.[4] Codifica apenas quatro proteínas: a proteína de maturação (proteína A ), a proteína de lise ( lys ), a proteína do capsídeo ( cp ) e a proteína replicase ( rep ).[1] O gene que codifica a lys sobrepõe-se tanto à extremidade 3' do gene upstream( cp ) quanto à extremidade 5' do gene downstream ( rep ), e foi um dos primeiros exemplos conhecidos de genes sobrepostos . O genoma de RNA de fita positiva serve como RNA mensageiro e é traduzido após a desnudação viral dentro da célula hospedeira. Embora as quatro proteínas sejam codificadas pelo mesmo RNA mensageiro/viral, elas não são expressas nos mesmos níveis.
Ver também
Referências
- ↑ a b Calendar, ed. (2006). «Single-stranded RNA phages. Chapter 15». The Bacteriophages Second ed. [S.l.]: Oxford University Press. pp. 175–196. ISBN 978-0195148503
- ↑ Paranchych W, Graham AF (dezembro de 1962). «Isolation and properties of an RNA-containing bacteriophage». Journal of Cellular and Comparative Physiology. 60 (3): 199–208. PMID 13941371. doi:10.1002/jcp.1030600303
- ↑ Ni CZ, White CA, Mitchell RS, Wickersham J, Kodandapani R, Peabody DS, Ely KR (dezembro de 1996). «Crystal structure of the coat protein from the GA bacteriophage: model of the unassembled dimer». Protein Science. 5 (12): 2485–93. PMC 2143325
 . PMID 8976557. doi:10.1002/pro.5560051211
. PMID 8976557. doi:10.1002/pro.5560051211
- ↑ Fiers W, Contreras R, Duerinck F, Haegeman G, Iserentant D, Merregaert J, Min Jou W, Molemans F, Raeymaekers A, Van den Berghe A, Volckaert G, Ysebaert M (abril de 1976). «Complete nucleotide sequence of bacteriophage MS2 RNA: primary and secondary structure of the replicase gene». Nature. 260 (5551): 500–7. Bibcode:1976Natur.260..500F. PMID 1264203. doi:10.1038/260500a0
Ligações externas
- Genoma completo (incluindo os isolados R17, DL16 e J20 )